Modelos Epidemiológicos: mudanças entre as edições
| Linha 83: | Linha 83: | ||
== Implementação == | == Implementação == | ||
Os códigos foram | Os códigos da simulação foram implementados na linguagem [https://en.wikipedia.org/wiki/C_(programming_language) C], para a visualização foi utilizada a linguagem [https://pt.wikipedia.org/wiki/Python Python]. | ||
=== Implementação modelo SIR === | === Implementação modelo SIR === | ||
| Linha 90: | Linha 90: | ||
=== Implementação modelo SIR com quarentena voluntária === | === Implementação modelo SIR com quarentena voluntária === | ||
Algumas modificações são realizadas no código anterior: a probabilidade do indivíduo passar de suscetível a infectado depende da escolha pela quarentena e é adicionada a parte da escolha individual. | Algumas modificações são realizadas no código anterior: a probabilidade do indivíduo passar de suscetível a infectado depende da escolha pela quarentena e é adicionada a parte da escolha individual. | ||
| Linha 150: | Linha 148: | ||
} | } | ||
</source> | </source> | ||
=== Visualização === | |||
#!/usr/bin/env python3 | |||
# -*- coding: utf-8 -*- | |||
""" | |||
Graficos - trabalho | |||
""" | |||
import matplotlib.pyplot as plt | |||
import pandas as pd | |||
import numpy as np | |||
from matplotlib import animation | |||
#%% Read data | |||
data = pd.read_csv('./output.txt', | |||
sep=" ", index_col=False) # sir x tempo | |||
data.sort_values(by='t', ascending=True, inplace=True) | |||
data.set_index('t', inplace=True) | |||
data_j = pd.read_csv('./output_jogo.txt', | |||
sep=" ", index_col=False) # sir x tempo | |||
data_j.sort_values(by='t', ascending=True, inplace=True) | |||
data_j.set_index('t', inplace=True) | |||
#%% Visualization | |||
data['total'] = data['r'] + data['i'] + data['s'] | |||
#%% SIR versus time | |||
plt.title('Evolução temporal da doença') | |||
data = data / data['s'][0] # normalização da população | |||
# data_j = data_j / data_j['s'][0] # normalização da população | |||
plt.plot(data['r'], label='R') | |||
plt.plot(data['s'], label='S') | |||
plt.plot(data['i'], label='I') | |||
# data_j = data_j / data_j['s'][0] # normalização da população | |||
# plt.plot(data_j['r'], label='R jogo') | |||
# plt.plot(data_j['s'], label='S jogo') | |||
# plt.plot(data_j['i'], label='I jogo') | |||
plt.ylabel('Fração da população') | |||
plt.xlabel('Tempo') | |||
plt.grid() | |||
plt.legend() | |||
#%% Dinamica da quarentena voluntaria | |||
dmc_loc = np.loadtxt('./dados/output_dinamica_loc.txt') # lê o arquivo | |||
#%% | |||
L = int(np.sqrt(np.shape(dmc_loc)[1])) | |||
# forma uma malha LxL, pra poder plotar como se fosse x - y - z | |||
x = y = np.arange(0, L, 1) | |||
xv, yv = np.meshgrid(x, y) | |||
def animate(i): | |||
plt.clf() # limpa a figura, pra nao ficar sobrepondo figs | |||
# # titulos | |||
plt.suptitle('Evolução da dinâmica de quarentenados', fontsize=14) | |||
plt.title(f'Tempo: {i}', fontsize=10) | |||
quarentena = np.zeros(shape=(L, L)) | |||
for j in range(L): | |||
quarentena[j] = dmc_loc[i, j*L : (j+1) * L] | |||
# # plot | |||
graph = plt.scatter(xv,yv, c= quarentena, marker='.', vmax=1.0, vmin=0.0) | |||
return graph | |||
fig, ax = plt.subplots() | |||
ani = animation.FuncAnimation(fig, animate, frames = len(dmc_loc), repeat=False, interval=5) | |||
#%% Reorganiza para plot da quantidade por tempo | |||
quarentena, nao_quarentena = [], [] | |||
for i in range(len(dmc_loc)): | |||
quarentena.append(len(np.where(dmc_loc[i] == 0)[0])/2500) # aqui trocar o divisor por L*L | |||
nao_quarentena.append(len(np.where(dmc_loc[i] == 1)[0])/2500) # aqui trocar o divisor por L*L | |||
#%% Evolução da quantidade de quarentenados e infectados | |||
fig, ax = plt.subplots() | |||
ax2 = ax.twinx() | |||
plt.title('Evolução da quantidade de quarentenados e infectados') | |||
ax.plot(quarentena, label='QT', color='black', alpha=0.8) | |||
# ax.plot(nao_quarentena, label='QN', color='red', alpha=0.6) | |||
# ax.set_ylim(0, 1600*1.5) | |||
ax2.plot(data['i'], label='I') | |||
# ax.plot(data['r'], label='I') | |||
# ax.plot(data['s'], label='I') | |||
ax.legend(loc='lower left') | |||
# ax2.legend(loc='lower right') | |||
== Resultados == | == Resultados == | ||
Edição das 21h39min de 22 de novembro de 2021
Em construção
Grupo: Gabriel Schmökel, Julia Remus e Luis Gustavo Lang Gaiato
O objetivo do trabalho é realizar a implementação do modelo SIR e de um modelo simplificado do proposto pelo artigo "An epidemiological model with voluntary quarantine strategies governed by evolutionary game dynamics" [1] utilizando Monte Carlo.
Será apresentada uma breve introdução sobre o tema e as equações que envolvem o desenvolvimento dos cálculos, as implementações e seus respectivos resultados.
Introdução
O objetivo do trabalho é realizar a implementação do modelo SIR e de um modelo simplificado do proposto pelo artigo "An epidemiological model with voluntary quarantine strategies governed by evolutionary game dynamics" [1] utilizando Monte Carlo.
O modelo apresentado por Marco Amaral, et al [1] propõe que o indivíduo escolha fazer a quarentena dependendo do risco que observa a partir da quantidade de infectados no sistema. Acoplada à escolha pela quarentena está o modelo SIR com parâmetros distintos para indivíduos não isolados e isolados. Para realizar a simulação os autores utilizam a teoria de campo médio, obtendo ondas de infecção ao longo do tempo.
Neste trabalho, a escolha do indivíduo pela quarentena se dará de acordo com o estado do seus vizinhos mais próximos - utilizado o dilema do prisioneiro -, enquanto a evolução dos infectados no sistema será realizada com o modelo SIR tal como na referência citada. Para a simulação foi utilizado o método de Monte Carlo.
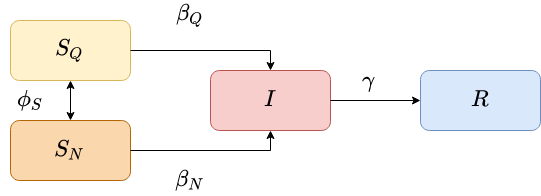
O esquemático do modelo SIR com a escolha da quarentena pode ser visto na seção Modelo SIR com quarentena voluntária.
Modelos
Modelo SIR
Esse modelo propõe dividir a população em três categorias:
- Susceptível (S): um componente susceptível é aquele que ainda não passou e não possui a doença, mas poderá ser infectado em contato com I.
- Infectado (I): um componente infectado com a doença.
- Recuperado ou Removido (R): aquele que já passou pela doença e já está recuperado dela com imunidade (não pegará novamente); pode ser utilizado o compartimento como sendo de removidos, com o cuidado de retirá-los da simulação.
Modelo SIR com quarentena voluntária
No esquemático pode-se ver o modelo utilizado no trabalho, ele é uma simplificação do artigo escrito por Amaral, et al [1]. Nele temos:
- Componentes suscetíveis podem estar ou não em quarentena. A probabilidade para a escolha da quarentena ocorrer depende de quantos infectados há nos vizinhos.
- Ao escolher estar ou não em quarentena, esses componentes tem probabilidades diferentes de adquirir a doença ( e ) e se tornar infectados.
- Infectados possuem a mesma probabilidade de se tornarem recuperados.
- Após recuperados da doença, as pessoas não conseguem adquiri-lá novamente.
- Todos os indivíduos escolhem estar ou não isolados, modificando a escolha do vizinho, mas somente a quarentena dos suscetíveis afeta a evolução SIR.
Para simular a quarentena voluntária é utilizado o jogo definido pelo Dilema do Prisioneiro. Esse dilema descreve a situação onde dois condenados (A e B) precisam decidir se colaboram ou não sem saber a decisão do seu par. Para isso temos 4 possibilidades: A e B colaboram (ambos saem com uma recompensa R), A colabora mas B não colabora (B ficaria com o valor da tentação T e A com o custo do sonso S), o caso contrário onde A não colabora e B colabora e A e B não colaboram (ambos ganham com uma penalidade P). [2]
Essas possibilidades podem ser resumidas em uma matriz de perdas e ganhos (matriz de payoff):
| A coopera | A não coopera | |
|---|---|---|
| B coopera | R / R | S / T |
| B não coopera | T / S | P / P |
Os valores da matriz payoff devem obedecer a ordem T > R > P > S. Além disso, para simulações com várias iterações deve ser obedecido que 2R > T + S. [2]
A proposta de observar a evolução da infecção dependendo da quarentena precisa utilizar mais de um par de interagentes, por isso é definido uma rede onde cada componente possui um ponto fixo. A partir disso, cada um desses componentes interagem com seus quatro vizinhos mais próximos (para os pontos do contorno é utilizado que as bordas são unidas por condições de contorno periódicas). [2]
Segundo Hauert e Szabó [2], os colaboradores tendem a ser extintos em jogos que consideram a interação aleatória, independente da sua concentração inicial, ou seja, todos tendem a não ganhar nada (não colaborar mutuamente) a fim de reduzir custos. Enquanto isso, se for proposto que um componente só escolhe uma estratégia conforme seus vizinhos, é visto é a formação de clusters de cooperadores e de não cooperadores; com isso, os componentes que estão na borda desses espaços, ganham na interação com os vizinhos colaboradores e perdem com a outra interação.
Esse jogo de quarentena é acoplado ao sistema SIR anteriormente descrito. A única diferença para o SIR sem o jogo é que as probabilidades de um componente S se tornar infectado mudam a partir do seu estado de quarentena.
Implementação
Os códigos da simulação foram implementados na linguagem C, para a visualização foi utilizada a linguagem Python.
Implementação modelo SIR
Talvezzzz: Usar essa Analytical solution of SIR-model [3] pra verificar se o código funciona
Implementação modelo SIR com quarentena voluntária
Algumas modificações são realizadas no código anterior: a probabilidade do indivíduo passar de suscetível a infectado depende da escolha pela quarentena e é adicionada a parte da escolha individual.
A função do jogo (escolha pelo isolamento) é definido abaixo.
void jogo(int t){
/*
Dinâmica da escolha voluntária do quarentenado ou não
*/
int sitio, i, j, k;
double prob;
double sums, sumv;
int vizinho, dir;
for (i=0;i<L2;i++){
sitio = FRANDOM * L2;
dir = FRANDOM * 4 + 1;
vizinho = viz[sitio][dir];
sums = 0;
sumv = 0;
for(j=1 ; j < 5 ; j++) {
sums += payoff[dmc_quarentena[sitio]][dmc_quarentena[viz[sitio][j]]];
sumv += payoff[dmc_quarentena[vizinho]][dmc_quarentena[viz[vizinho][j]]];
}
prob = 1.0 / (1.0 + exp(-(sumv - sums) / TEMP ));
if(FRANDOM > prob) {
dmc_quarentena[sitio] = dmc_quarentena[vizinho];
}
}
// Escreve o estado de quarentena no arquivo, cada tempo uma linha
FILE *dmcfile;
char output2[10000];
sprintf(output2, "output_dinamica_loc.txt");
dmcfile = fopen(output2,"a");
for(k=0; k<L2; k++){
fprintf(dmcfile," %d ", dmc_quarentena[k]);
}
fprintf(dmcfile," \n ");
fclose(dmcfile);
return;
}
Visualização
- !/usr/bin/env python3
- -*- coding: utf-8 -*-
""" Graficos - trabalho """
import matplotlib.pyplot as plt import pandas as pd import numpy as np from matplotlib import animation
- %% Read data
data = pd.read_csv('./output.txt',
sep=" ", index_col=False) # sir x tempo
data.sort_values(by='t', ascending=True, inplace=True)
data.set_index('t', inplace=True)
data_j = pd.read_csv('./output_jogo.txt',
sep=" ", index_col=False) # sir x tempo
data_j.sort_values(by='t', ascending=True, inplace=True)
data_j.set_index('t', inplace=True)
- %% Visualization
data['total'] = data['r'] + data['i'] + data['s']
- %% SIR versus time
plt.title('Evolução temporal da doença')
data = data / data['s'][0] # normalização da população
- data_j = data_j / data_j['s'][0] # normalização da população
plt.plot(data['r'], label='R') plt.plot(data['s'], label='S') plt.plot(data['i'], label='I')
- data_j = data_j / data_j['s'][0] # normalização da população
- plt.plot(data_j['r'], label='R jogo')
- plt.plot(data_j['s'], label='S jogo')
- plt.plot(data_j['i'], label='I jogo')
plt.ylabel('Fração da população') plt.xlabel('Tempo')
plt.grid()
plt.legend()
- %% Dinamica da quarentena voluntaria
dmc_loc = np.loadtxt('./dados/output_dinamica_loc.txt') # lê o arquivo
- %%
L = int(np.sqrt(np.shape(dmc_loc)[1]))
- forma uma malha LxL, pra poder plotar como se fosse x - y - z
x = y = np.arange(0, L, 1)
xv, yv = np.meshgrid(x, y)
def animate(i):
plt.clf() # limpa a figura, pra nao ficar sobrepondo figs
# # titulos
plt.suptitle('Evolução da dinâmica de quarentenados', fontsize=14)
plt.title(f'Tempo: {i}', fontsize=10)
quarentena = np.zeros(shape=(L, L))
for j in range(L):
quarentena[j] = dmc_loc[i, j*L : (j+1) * L]
# # plot
graph = plt.scatter(xv,yv, c= quarentena, marker='.', vmax=1.0, vmin=0.0)
return graph
fig, ax = plt.subplots() ani = animation.FuncAnimation(fig, animate, frames = len(dmc_loc), repeat=False, interval=5)
- %% Reorganiza para plot da quantidade por tempo
quarentena, nao_quarentena = [], []
for i in range(len(dmc_loc)):
quarentena.append(len(np.where(dmc_loc[i] == 0)[0])/2500) # aqui trocar o divisor por L*L nao_quarentena.append(len(np.where(dmc_loc[i] == 1)[0])/2500) # aqui trocar o divisor por L*L
- %% Evolução da quantidade de quarentenados e infectados
fig, ax = plt.subplots()
ax2 = ax.twinx()
plt.title('Evolução da quantidade de quarentenados e infectados')
ax.plot(quarentena, label='QT', color='black', alpha=0.8)
- ax.plot(nao_quarentena, label='QN', color='red', alpha=0.6)
- ax.set_ylim(0, 1600*1.5)
ax2.plot(data['i'], label='I')
- ax.plot(data['r'], label='I')
- ax.plot(data['s'], label='I')
ax.legend(loc='lower left')
- ax2.legend(loc='lower right')
Resultados
Referências
- ↑ 1,0 1,1 1,2 1,3 AMARAL, Marco; OLIVEIRA, Marcelo de; JAVARONE, Marco, An epidemiological model with voluntary quarantine strategies governed by evolutionary game dynamics. arXiv:2008.05979v2 [physics.soc-ph] .
- ↑ 2,0 2,1 2,2 2,3 HAUERT, Christoph; SZABÓ, György. Game theory and physics. DOI: 10.1119/1.18485144 .
- ↑ Analytical solution of SIR-model